DNA 응용 기술 동향
DNA Application Technology Trends
- 저자
- 이재호, 김도영, 박문호, 최윤호, 박윤옥 / 씨앗기술연구실
- 권호
- 32권 2호 (통권 164)
- 논문구분
- 미래전략기술 특집
- 페이지
- 29-36
- 발행일자
- 2017.04.01
- DOI
- 10.22648/ETRI.2017.J.320204
 본 저작물은 공공누리 제4유형: 출처표시 + 상업적이용금지 + 변경금지 조건에 따라 이용할 수 있습니다.
본 저작물은 공공누리 제4유형: 출처표시 + 상업적이용금지 + 변경금지 조건에 따라 이용할 수 있습니다.- 초록
- 본고에서는 바이오 기술(BT: Bio Technology)의 주요 소재인 DNA(DeoxyriboNucleic Acid, 디옥시리보핵산)를 정보기술(IT: Information Technology)과 나노 기술(NT: Nano Technology)에 적용한 세 가지 DNA 응용 기술 동향에 대해 소개하였다. 먼저 1958년 프랜시스 크릭(Francis Crick)이 주장한 센트럴 도그마(Central Dogma)의 출발점인 DNA의 구조와 기능에 대해 최대한 자세히 소개하였고, DNA의 염기 서열 방식을 이용한 DNA 저장장치에 관해 설명하였다. 그다음 장에서는 DNA의 자기 조립(Self-Assembly) 능력과 자기 복제 능력 및 다른 분자를 인식하여 결합하는 특성을 정보기술에 적용한 DNA 컴퓨터에 대해 설명하였다. 마지막으로, 나노 단위의 DNA 구조를 응용한 나노 기술 중에서 다양한 나노구조물을 만드는 기술인 DNA 오리가미 기술에 대해 설명하였다.
Share
Ⅰ. 서론
생화학 분야와 분자생물학의 많은 과학자들은 부모의 얼굴 모양, 혈액형 그리고 눈동자의 홍채 색 같은 특징 혹은 형질이 세포 안의 어떤 물질을 통해 어떻게 다음 세대에 완벽하게 복제되어 전달될 수 있는지에 대해 오랫동안 연구해 왔다. 예를 들면 유전 형질은 부모에게서 자손에게로 대대로 전달된다. 몇 세대 전에 있었던 형질이 사라졌다가 후대에 다시 나타나는 불규칙적인 현상인 격세유전(Atavisim) 때문에 초기 유전자 연구에 많은 어려움이 있었지만, 프랜시스 크릭(Francis Crick)과 제임스 왓슨(James Watson)이 1953년에 DNA(Deoxyribo Nucleic Acid)의 이중 나선(Dual Helix) 구조를 밝히면서 DNA 연구는 급진전되었다[1]. 결국, 혈액형과 같은 유전형질을 전달하는 것은 세포핵 안에 존재하는 염색체 그중에서도 핵산의 일종인 DNA임이 밝혀졌다. 즉, DNA의 비주기적인 1차원 염기 서열(배열)이 유전자이며, 염색체에 DNA 염기 서열(배열)이라는 형태로 압축되어 있으며, 그 DNA 염기 서열이 후대로 전달되는 것임이 밝혀졌다[2].
여기서 한 걸음 더 나아가, 1990년에 인간의 약 30억개의 염기쌍(BP: Base-Pair)의 DNA 염기 서열을 파악하려는 게놈 프로젝트(Genome Project)를 영국, 독일, 프랑스, 미국 그리고 일본 5개국이 공동으로 15년 계획으로 시작하였으며, 2001년에 모든 염기 순서를 밝혀냈다. DNA 염기 서열에 따라 단백질을 구성하는 아미노산의 서열이 결정되며, 이렇게 결정된 아미노산 서열의 단백질 때문에 다양한 종류의 단백질이 존재한다. 일 예로, 빈혈 증세를 보이는 겸상적혈구빈혈증(Sickle-Cell Anemia)이라는 병을 앓고 있는 환자들은 산소를 운반하는 역할을 하는 적혈구 안의 헤모글로빈 단백질의 모양이 보통 사람들과 다르며, 그 이유는 헤모글로빈 단백질의 아미노산 서열 중 정상적인 글루탐산(Glutamic Acid, Glu) 대신 발린(Valine, Val)으로 이루어졌기 때문이다. 즉, 손상된 DNA 염기 서열에 의해 아미노산 서열이 다르게 배열된 것이다. 이와 같이, 염기의 순서를 다 알았다는 것과 서열의 뜻을 안다는 것은 전혀 다른 문제이며, 계속해서 병의 원인을 유전적인 측면에서 밝히고자 하는 노력이 진행되고 있다. 즉, 염기 서열의 뜻을 해석하려고 많은 연구를 하고 있다.
본고에서는 지금까지 밝혀진 DNA의 구조와 기능에 대해 Ⅱ장에서 조금 더 상세히 설명한다.
DNA는 유전 정보의 저장 및 복제가 가능하다는 측면에서 견고한 하드 디스크에 비유될 수 있으며, 인공적으로 DNA 염기 서열을 합성(Synthesis)하는 기술의 발달로 인해 DNA를 저장 장치로 활용하는 연구에 대해 Ⅲ장에서 자세히 설명한다.
Ⅳ장에서는 여러 단백질과 DNA와의 상호 작용으로 인해 자기 복제 및 자기 조립(self-assembly) 특성을 이용한 DNA 컴퓨터에 대하여 설명한다. DNA는 단백질이 필요한 순간에 단백질 합성에 필요한 정보를 가지고 있는 단백질 데이터베이스에 비유할 수 있으며, 주변의 여러 단백질과 온도 그리고 화학물질의 농도에 따라 단백질을 합성하라는 메시지를 처리하는 연산 장치 역할을 수행한다고 생각할 수 있다.
Ⅴ장에서는 DNA를 나노 기술(NT)에 적용한 DNA 오리가미 나노 기술에 대해서 설명한다. 기본적으로 DNA는 나노 스케일이므로 자연스럽게 나노 기술에 쉽게 적용할 수 있다.
마지막으로, 결론에서는 지금까지 DNA를 활용한 세 가지 DNA 응용 기술에 대하여 요약 및 정리하였다.
Ⅱ. DNA 개요
Ⅱ장에서는 DNA 구조와 DNA가 어떤 기능을 하는지에 대해서 생물학적으로 너무 깊이 들어가지 않는 선에서 최대한 자세히 살펴 본다.
1. DNA 구조
세포(Cell) 안에는 핵막으로 둘러 쌓인 핵이 있고, 그핵 안에 염색체(Chromosome)가 있다. 염색체는 항상 보이지는 않고 세포가 분열하기 전에 잠깐 보이는데, DNA와 몇 가지 단백질로 구성된 가느다란 실 같은 염색사(Chromatin Thread)가 풀어져 있다가 세포분열 전에 염색사가 뭉쳐서 굵은 다발이 되는데, 이것이 염색체이다. 사람의 염색체는 46개(23쌍)의 염색체가 있으며 남자는 44개와 XY 염색체를 가지며 여자는 44개와 XX 염색체를 가진다.
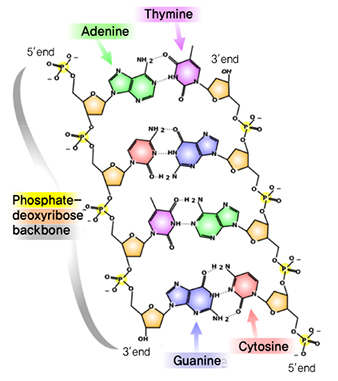
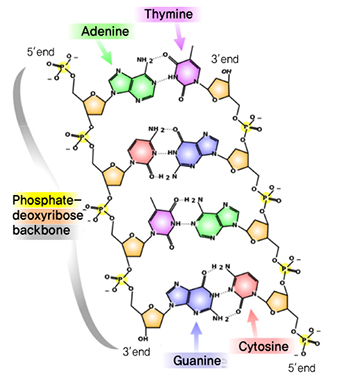
(그림 1)과 같이 DNA는 기본 단위는 염기(Base), 5개의 탄소로 구성된 디옥시리보스(Deoxyribose, 갈색 오각형) 그리고 인산기(P: Phosphate, 노란색)가 결합된 뉴클레오타이드(Nucleotide)이다. DNA를 구성하는 염기에는 아데닌(A: Adenine), 티민(T: Thymine), 시토신(C: Cytosine) 그리고 구아닌(G: Guanine) 이렇게 4종류가 있기 때문에 뉴클레오타이드도 4종류이다[2].
(그림 1)에서 보면 2개의 수소 결합으로 A-T가 짝을 이루며, 3개의 수소 결합으로 G-C가 쌍을 이루며 존재하는데, 이러한 결합이 DNA의 상보성이며, 이러한 상보성은 DNA의 정보를 복제하고 저장하는 기능을 수행한다. DNA를 구성하는 4종류의 염기(A, T, C, G)는 배열되는 서열에 따라 유전 정보가 결정되며, 염기가 배열된 순서에 따라 단백질을 만드는 아미노산 순서도 결정된다.
2. DNA 기능
우리 몸을 비롯한 모든 생명체는 다양한 세포로 이루어져 있다. 피부와 뼈와 혈액 등을 구성하는 각각의 세포는 각 세포마다 독특하고 다양한 단백질을 생성하며 생명을 유지한다.
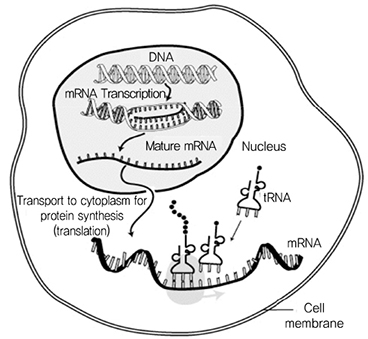
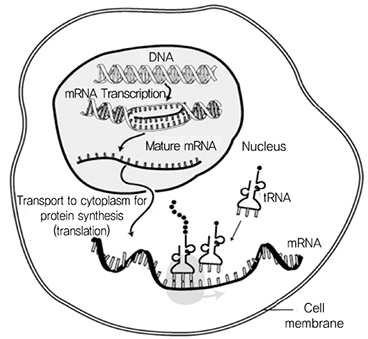
이렇게 다양한 단백질은 20가지의 아미노산(Amino Acid)으로 구성되며, 이 아미노산들이 펩타이드(Peptide) 결합으로 서로 길게 연결된 것을 폴리펩타이드(Poly-peptide)라고 하며, 폴리펩타이드보다 좀 더 크고 길게 연결된 중합체(Polymer)가 단백질이다. 각각의 단백질의 기능은 아미노산들의 배열 순서에 따라 결정되며, 앞서 설명한 바와 같이 DNA 염기 서열에 의해서 결정된다. DNA로부터 단백질을 생성하며 순서는 (그림 2)와 같고 아래 세 가지 과정을 거친다[3].
• 복제(Replication): 핵 속에서 DNA 이중나선의 일부분이 열림.
• 전사(Transcription): DNA의 유전 정보를 읽은 뒤 유연하고 활용하기 쉬운 전령 RNA(mRNA: messenger RNA)를 만듬.
• 번역(Translation): 핵공(Nuclear Pore)을 통과해 핵 밖으로 나온 전령 RNA가 단백질 합성 기계인 리보솜(Ribosome)에 붙고, 리보솜은 전령 RNA의 코돈(Codon)을 바탕으로 아미노산 중합체인 단백질을 만듬. 운반 RNA(tRNA: transfer RNA)는 아미노산을 리보솜으로 운반함.
Ⅲ. DNA 저장 장치
1. 배경
데이터베이스(DB: DataBase) 혹은 비정형의 데이터로부터 가치 있는 정보를 추출하고 결과를 분석하는 기술인 빅 데이터(Big Data) 시대를 맞이하였다. 의료, 과학 그리고 경제 분야 등 다양한 분야에서 중요성이 부각되고 있는 인공지능도 기본적으로 이러한 방대한 빅 데이터를 이용한다.
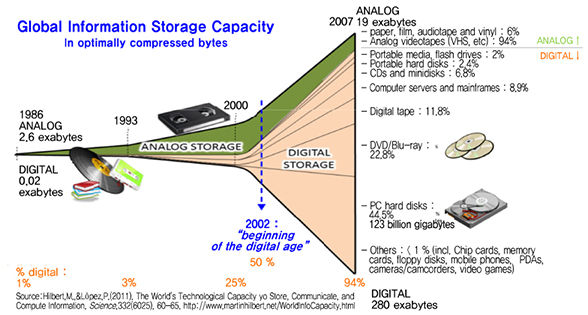
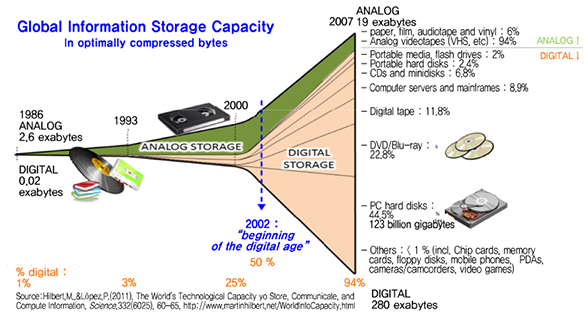
시장조사기관 IDC 예측에 따르면 2020년까지 전 세계 디지털 데이터는 40 zeta byte(1 zeta byte=1021 byte)로 확대될 전망이며[4], (그림 3)처럼 시간이 흐름에 따라 아날로그 저장 장치에서 DVD나 하드디스크드라이브(HDD: Hard Disk Drive) 같은 디지털 저장 장치로 빠르게 전환되고 있다.
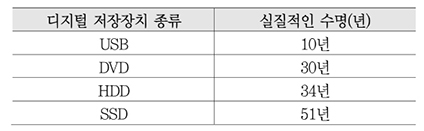
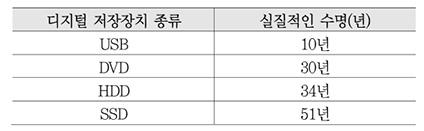
디지털 저장 장치는 쉽게 기록하고 저장할 수 장점이 있지만, <표 1>처럼 저장 수명이 짧은 게 단점이다. 이론적으로 DVD나 SSD(Solid State Drive) 같은 저장 장치는 최대 100년을 사용할 수 있지만, 현실적으로는 물리적 특성 때문에 이보다 훨씬 수명이 짧다.
또 다른 문제점은, 수많은 디지털 저장 장치를 사용하는 데이터센터의 운용 및 유지 비용이다. 한국IT서비스산업협회에서 실시한 ‘데이터센터 산업 육성을 위한 기반조성 연구•조사’에 따르면 디지털 저장 장치를 사용하여 데이터센터를 운용하고 있는 상황에서 제일 시급한 문제점은 전기 요금이다. 데이터센터를 24시간 운영해야 하는 상황에서 저장 장치에서 발생하는 열을 식히기 위한 냉방 비용 및 저장 장치를 설치하는 데 필요한 공간 확보 등 여러 애로사항을 정부가 지원해 주길 원하고 있다[5].
이러한 상황에서 반영구적이고, 데이터를 저장하고 보관하는데 전기료와 같은 유지비용이 적게 드는 DNA를 활용한 저장 방법이 주목을 받고 있다. DNA 저장 장치의 또 다른 장점은 대용량의 데이터를 적은 양의 DNA로 저장할 수 있다는 것이다. 과학 전문지 『뉴 사이언티스트』에 의하면 1g의 DNA는 이론적으로 현재 구글과 페이스북을 포함한 모든 정보기술기업이 보유한 데이터를 저장할 수 있다[6].
또한, DNA 저장 장치가 주목을 받는 이유 중 하나는 DNA 염기 서열을 인공적으로 합성하는 DNA 합성(DNA synthesis) 기술과 DNA 염기 서열을 읽는 시퀀싱(Sequencing) 기술이 비약적으로 발전했기 때문이다. DNA 합성 기술은 데이터를 쓰는 기술이며, 시퀀싱 기술은 데이터를 읽는 기술이다. 그중 DNA 합성 기술은 V장의 DNA 나노 기술에서도 사용된다.
2. 기본원리
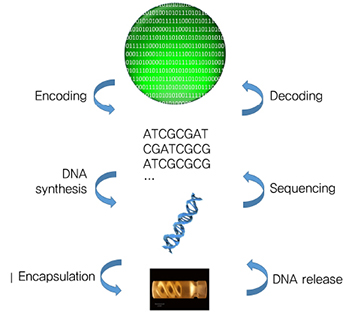
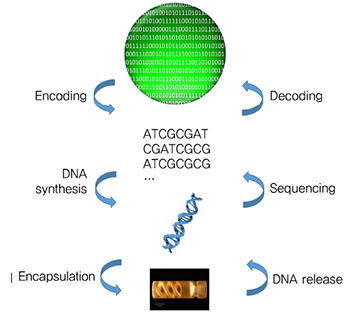
0과 1로 이루어진 디지털 정보를 DNA를 이용하여 저장하는 DNA 저장 장치의 동작 원리는 (그림 4)와 같다[6].
앞서 Ⅱ장에서 설명한 대로 DNA는 네 가지 염기(A, T, C, G)로 구성되어 있는데, A는 T와 G는 C와 각각 상보적으로 결합하는 구조를 가지므로 A와 T의 결합은 0으로, C와 G의 결합은 1로 설정하여 0과 1의 디지털 정보를 DNA 염기 서열로 인코딩한다. 이렇게 인코딩된 DNA 염기 서열은 기계에서 DNA 합성을 통해 인위적으로 만들어지고, 캡슐화(Encapsulation)하여 데이터를 저장한다.
데이터를 읽는 과정은 이와 반대 과정을 통해 이루어진다. 먼저 캡슐을 제거(DNA release)하고 DNA 해독 장치로 DNA 염기 서열을 읽는다(Sequencing). 이렇게 읽은 염기 서열을 다시 0과 1로 번역하면 원래의 데이터와 동일하게 데이터를 복원할 수 있다.
3. R& D 연구 현황
DNA 저장 장치에 대한 R& D는 해외에서 활발히 연구가 진행 중이다.
2012년에 미국 하버드 의학대학원의 교수이며 유전체학 분야의 전문가인 조지 처치(George Church)는 책 1권을 DNA 1mg에 저장한 후 3개월 후에 DNA 메모리에서 책 내용을 복원하는 데 성공하였다[7].
영국의 Oxford Nanopore Technologies 회사는100g미만의 USB 3.0의 인터페이스를 가진 USB 크기의 DNA sequencer인 MinION을 개발하였으며, 2015년 세계경제포럼(World Economic Forum)에도 소개되었다. 해당 홈페이지(https://nanoporetech.com/products/minion)에서 MinION을 사용하여, 데이터를 읽고 쓰는 과정을 동영상을 통해 볼 수 있다.
2016년 7월에 마이크로소프트(Microsoft)와 미국의 워싱턴 대학이 함께 200MB 상당의 저장 용량 개발하였으며[8], DNA를 인위적으로 합성하여 대량의 데이터를 저장할 수 있는 기술을 개발하는 트위스트 바이오사이언스(Twist Bioscience) 회사에 자금을 투자하여 연구 체제를 구축하는 데 합의하였다[4].
지금까지 살펴본 성공적인 사례를 보면 많은 성과가 있었지만, 앞으로 데이터를 읽고 쓰는 속도 및 에러 정정 향상 등 많은 분야에서 추가로 성능 개선에 대한 연구가 더 필요하다.
Ⅳ. DNA 컴퓨터
1. 배경
현재 사용되고 있는 컴퓨터는 CPU(Central Processing Unit), 메모리 그리고 프로그램으로 구성된 폰노이만 구조이다. 이러한 방식의 컴퓨터는 프로그램에 의해 계산을 순차적으로 수행하며, 주소에 의해 메모리에 순차적으로 접근해서 데이터를 읽고 저장하는데, 고속 컴퓨터에서 이러한 순차적 처리 방법 때문에 병목 현상이 발생하는 문제점이 있다[9].
반면, 인간의 뇌는 많은 뉴런이 동시에 연산에 참여하는 병렬적인 계산 방식을 사용하며, 주소 기반이 아닌 연상 능력을 이용하여 문제를 해결할 뿐만 아니라, 에너지 소모도 거의 없다. 이러한 인간의 뇌의 동작 방식을 CPU에 적용한 것이 뉴로모픽(Nuromorphic)칩이다. 인텔은 2012년에 뉴로모픽칩 설계를 공개했으며, 2013년 퀄컴은 뉴로포픽칩과 유사한 제로스(Zeroth) 프로세서를 발표했다. 하지만, 이러한 뉴로모픽칩 또한 실리콘을 사용하기 때문에, 집적화에 따른 발열과 양자역학의 불확정성 원리에 의한 누전 등 많은 문제점을 내포하고 있으므로 성능의 한계가 존재한다.
따라서, 실리콘 컴퓨터 시대 이후를 대비하기 위하여 유전적 정보를 담고 있는 DNA를 컴퓨터에 적용하는 연구가 1994년 컴퓨터 공학자 아들만(Leonardo M. Adleman)에 의해서 시작되었다.
2. 기본원리
기존의 컴퓨터에서 사용하는 사칙연산 연산자와는 달리 DNA 컴퓨터는 생체 분자를 이용하기 때문에 분자 생물학 실험에서 사용하는 여러 가지 연산 도구를 사용하며 아래와 같다[10].
• 하이브리드형성(Hybridization)
• 중합효소 연쇄반응(PCR: Polymerase Chain Reaction)
• 항체 친화력 반응(Antibody affinity)
• 여러 가지 효소(Enzyme)들
3. R& D 연구 현황
2013년 3월에 Stanford 대학의 드류 앤디(Drew Endy)가 이끄는 Bioengineer 팀이 트랜스크립터(Transcriptor) 개발을 발표하였다. 트랜스크립터는 DNA로 구성된 실리콘으로 비유하자면 트랜지스터 같은 장치이며, 기존의 컴퓨터 사칙연산과 같은 AND, OR, NOR 그리고 XNOR 등과 같은 연산 수행이 가능한 소자이다[11].
국내의 서울대학교 컴퓨터공학부 장병탁 교수는 DNA 컴퓨터를 만들어 인공지능의 성능을 향상하기 위한 인공지능 학습에 활용하고 있다. 우선 DNA 염기 서열을 재구성해 특정한 문자나 수식을 표현하는 구조를 만든 다음, 학습을 통해 새로운 정보를 기존 DNA 옆에 합성하거나, 사이에 삽입하는 방식으로 마치 컴퓨터가 스스로 연관성이 높은 정보끼리 모으고 분류하는 식으로 작동한다는 것이다[8].
아직 실리콘 기반의 컴퓨터를 대체할 만한 가시적인 성과가 미흡하지만, 계속해서 DNA 컴퓨터 관련하여 많은 연구가 진행되고 있으므로, 실리콘 이후 시대를 위한 DNA 컴퓨터도 상용화가 될 것으로 예상한다.
Ⅴ. DNA 나노 기술
1. 배경
DNA 나노 기술은, 4종류의 염기쌍들이 이중 혹은 삼중 수소 결합을 통해 안정적인 이중 나선 구조를 가지는 DNA 특성을 이용하여 나노미터 단위의 다양한 나노구조물을 만드는 기술이다. 즉, DNA를 단순히 유전정보의 저장 또는 전달 매체로 보지 않고 원하는 나노구조물을 만들기 위한 하나의 재료로 간주한 것이다. 이러한 DNA 나노 기술은 Ⅱ장에서 설명한 대로 DNA 합성 기술의 비약적인 발전에 힘입었다[12]. 1980년부터 지금까지 뉴욕대학교(NYU: New York University)의 네드리안 시만(Nadrian Seeman) 교수는 DNA 나노 기술 개발과 나노구조물을 만들기 위한 다양한 방법론적인 연구를 수행하였으며, 많은 나노구조물을 구현하였다.
2. 기본원리
DNA를 이용하여 나노 단위의 구조물을 제작하는 방법 중에서, 2006년에 캘리포니아 공과대학교 (Caltech: California Institute of Technology)의 폴 로데문드 (Paul Rothemund) 교수의 DNA 오리가미(origami) 나노 기술에 대해 설명한다[13]. 오리가미는 일본말로 종이접기를 뜻한다.
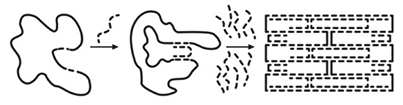
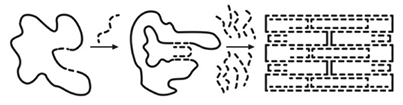
DNA 오리가미 나노 기술은 스캐폴드(Scaffold)와 스테이플(Staple)를 이용하여 열풀림(Thermal annealing)기법을 통해 나노구조물을 만들었다.
• 스캐폴드: 나노구조물을 만들기 위한 기본 골격으로 M13 박테리오파지에서 추출한 7,000개에서 8,000개 정도의 염기로 구성된 긴 환형 단일가닥(ss: single-stranded) DNA.
• 스테이플: 20개에서 50개 정도의 염기로 구성된 짧은 단일 가닥 DNA.
• 열풀림 기법: 80도 정도의 온도로 가열시킨 후 수 시간에서 수 십 시간 동안 서서히 온도를 낮추는 방법.
열풀림 방법을 사용하면 (그림 5)와 같이 스테이플 ((그림 5)의 중간의 점선)들이 스캐폴드((그림 5)의 왼쪽 실선)의 지정된 위치에 염기의 상보적 서열 결합을 하는 자기 조립(Self-assembly) 특성을 이용하여 DNA 나노구조물을 만들게 된다. 이러한 DNA 오리가미 기술은 타 나노공정 대비 비교적 단순하다는 장점이 있다.
(그림 5)
DNA 오리가미 제작 원리
[저자] Team Nanoscooter Braunschweig,
[출처] http://www.openwetware.org/wiki/Biomod/2014/ Design, CC BY-SA
이렇게 만들어진 2차원 나노구조물을 컴퓨터 프로그램을 이용하여 3차원 나노구조물로도 만들 수 있다. 컴퓨터 프로그램을 사용하는 이유는 사람이 일일이 7천개 이상의 염기 서열을 갖는 스캐필드를 실수 없이 정확히 설계하는 데는 한계가 있기 때문이다. 이때 사용하는 컴퓨터 프로그램 중에 가장 대표적으로 사용되는 프로그램은 하버드 대학 윌리엄 쉬(William Shih) 교수가 개발한, 3차원 랜더링 기능을 포함한 Cadnano (http://cadnano.org)이다.
3. R&D 연구 현황
(그림 6)과 같이 나노스쿠터 팀은 DNA 오리가미 기술과 8,064개의 뉴클레오타이드로 구성된 스캐폴드를 사용하여 3차원 나노스쿠터를 제작하였다.
(그림 6)
DNA 오리가미로 만든 3차원 구조물

[저자] Team Nanoscooter Braunschweig,
[출처] http://www.openwetware.org/wiki/Biomod/2014/Design, CC BY-SA
DNA를 이용한 다른 분야는 DNA 나노튜브 하이브리드이며, 이러한 새로운 방법을 이용함으로써 나노 튜브 및 화학적 센서 등 많은 분야에 도움이 될 것으로 기대된다[14].
Ⅵ. 결론
본고에서 바이오 기술의 주재료이며 우리에게 친숙한 유전자 DNA에 대해서 간략하게 설명하였으며, 정보 기술분야에서 DNA를 활용한 DNA 저장 장치와 DNA 컴퓨터에 대해서 살펴보았다. 또한, DNA가 나노 기술과 융합한 DNA 오리가미 기술을 설명하였다.
기존의 디지털 저장 장치에 비해 전력소모가 거의 없으며 오랫동안 저장할 수 있는 차세대 저장 장치인 DNA 저장 장치, 순차적으로 문제를 푸는 현재의 폰노이만 방식의 컴퓨터를 탈피하여 인간의 뇌와 유사하게 문제를 해결할 수 있는 DNA 컴퓨터 그리고 나노 단위의 DNA를 이용한 DNA 나노 기술 중 하나인 DNA 오리가미 기술에 대해 지속적인 관심과 투자 및 연구가 필요한 시점이다.
용어해설
센트럴 도그마(Central Dogma) 분자생물학의 중심원리로, 세 가지 전이 과정(복제, 전사, 번역)을 통해 DNA로부터 단백질 혹은 폴리펩타이드를 생성하는 원리를 설명
코돈(Codon) 3가지 염기로 구성된 뉴클레오타이드
약어 정리
BP
Base-Pair
BT
Bio Technology
CPU
Central Processing Unit
DNA
DeoxyriboNucleic Acid
HDD
Hard Disk Drive
IT
Information Technology
mRNA
messenger RNA
NT
Nano Technology
NYU
New York University
PCR
Polymerase Chain Reaction
RNA
RiboNucleic Acid
ss
single-stranded
SSD
Solid State Drive
tRNA
transfer RNA
장재은, “DNA 이중나선에 얽힌 드라마틱한 이야기,” 한겨례, 2008. 10. 15. http://www.hani.co.kr/arti/science/kistiscience/316103.html
곽노필, “꿈의 저장 장치 ‘DNA칩’시대 온다,” 한겨례, 2015. 3. 26. http://www.hani.co.kr/arti/economy/it/684076.html
박건형, “[IF] 생명 정보 담는 DNA가… 이젠 당신의 사진도 저장합니다,” 조선일보, 2016. 4. 30. http://news.chosun.com/site/data/html_dir/2016/04/22/2016042901932.html
S. Fisch, “Biological Transistor Enables Computing within Living Cells, Study Says,” Stanford Medicine News Center, Mar. 28th, 2013. https://med.stanford.edu/news/all-news/2013/03/biological-transistor-enables-computing-within-living-cells-study-says.html
곽민석, “DNA 나노 기술 및 소재의 기초와 생물리학적, 생의학적 응용,” BRIC View 동향 리포트, BRIC View 2015-T02, 2015. 1, pp. 1-12.
- Sign Up
- 전자통신동향분석 이메일 전자저널 구독을 원하시는 경우 정확한 이메일 주소를 입력하시기 바랍니다.